3D-MALDI-Imaging einer Rückenmarksverletzung bei der Ratte
| Arbeitsgruppe: | AG Technomathematik |
| Leitung: | Prof. Dr. Dr. h.c. Peter Maaß ((0421) 218-63801, E-Mail: pmaass@math.uni-bremen.de ) |
| Bearbeitung: |
Dr. Lena Hauberg-Lotte
Leïa Westerheide |
| Projektpartner: | Prof. Dr. Michel Salzet, PRISM, Université Lille |
| Laufzeit: | seit 01.02.2015 |

Die Darstellung der m/z Bilder m/z 772 (grün), m/z 768 (rot) und m/z 756 (blau) spiegelt die wichtigsten anatomischen Regionen des Rückenmarks wider, und zwar die graue und weiße Substanz sowie das dorsale Horn. Es wird deutlich, dass in der Läsionsstelle (L) des Rückenmarks die Struktur der Lipidverteilung nach 3 Tagen massiv gestört ist und auch die anatomischen Gegebenheiten des Rückenmarks nicht mehr zu erkennen sind. Bereits nach 7 Tagen sind jedoch eine Reorganisation der Lipidzusammensetzung und damit eine Regenerierung des Rückenmarks zu beobachten.
Seit einigen Jahren kooperiert die AG Technomathematik des ZeTeM mit Prof. Dr. Michel Salzet und Prof. Dr. Isabelle Fournier vom interdisziplinären Labor PRISM der Universität Lille. Der Schwerpunkt dieser Kooperation liegt auf der Analyse von dreidimensionalen MALDI-Imaging-Daten. Die gemeinsame Studie befasst sich mit neuroimmunologischen Fragestellungen bei Rückenmarksverletzungen der Ratte, aus denen auch Rückschlüsse auf den Menschen gezogen werden können. Verletzungen des Rückenmarks (vor allem durch Verkehrsunfälle, Stürze oder Sport) stellen auf Grund ihrer Häufigkeit und Schwere ein großes gesellschaftliches Gesundheitsproblem dar. Bei einer derartigen Verletzung ist das Ausmaß der Zerstörung des Rückenmarks von großer Bedeutung, wobei eine Läsion des Rückenmarks zur vollständigen Querschnittslähmung führen kann und immer von Entzündungsprozessen und Narbenbildung begleitet ist. Neue Studien zeigen nun, dass ausgehend von der Stelle der Läsion Regeneration des Gewebes möglich ist.
Diese Regenerationsprozesse sind Gegenstand unserer 3D-MALDI-Imaging-Analyse: Die Lipidverteilung im Rückenmark wurde sowohl räumlich, d.h. in drei Segmenten des Rückenmarks, als auch zeitlich, d.h. drei, sieben und zehn Tage nach Läsion, mittels bildgebender Massenspektrometrie untersucht. Eine große Herausforderung war dabei einerseits die große Datenmenge und andererseits die Registrierung der 324 Gewebeschnitte zu einem 3D-MALDI-Imaging-Modell. Derzeit ist SCiLS Lab von SCiLS, Zweigniederlassung der Bruker Daltonik GmbH (Bremen) die einzige kommerziell erhältliche Software weltweit, die in der Lage ist, derartige Daten zu analysieren und zu visualisieren.
Auf der mathematischen Seite wurden zahlreiche Algorithmen verwendet, um die 3D MALDI-Imaging-Daten auszuwerten und entscheidende Informationen zu erhalten: Am Anfang wurde standardmäßig eine Basislinienkorrektur mittels iterativer Konvolution sowie die Normalisierung mit TIC (Total Ion Count) durchgeführt. Anschließend wurden die relevanten Peaks durch Orthogonal Matching Pursuit detektiert und die Daten mit Hilfe des Bisecting k-means Algorithmus segmentiert. Um entscheidende m/z Werte aus den Daten zu extrahieren, die sowohl die räumlichen als auch die zeitlichen Unterschiede der Proben charakterisieren, wurden mittels Korrelationsanalyse m/z-Werte detektiert, die z.B. mit der grauen bzw. weißen Substanz des Rückenmarks sowie mit der Läsionsstelle kolokalisiert vorliegen. Außerdem führte die ROC-Analyse (Receiver Operating Characteristics) zur Detektion von m/z-Werten, die innerhalb der Daten zwischen den unterschiedlichen Zeitpunkten, Segmenten bzw. anatomischen Regionen diskriminieren.
Die Untersuchung der Rückenmarksverletzung mittels 3D-MALDI-Imaging konnte bestätigen, dass die Lipidzusammensetzung innerhalb der Läsionsstelle durch die Verletzung stark beeinflusst ist, da keine anatomische Struktur des Rückenmarks mehr zu erkennen war. Darüber hinaus wurde jedoch gezeigt, dass bereits nach sieben Tagen die Regeneration des Rückenmarks einsetzt, was im MALDI Imaging in einer deutlichen Reorganisation der Lipide innerhalb der Läsionsstelle sichtbar ist. Diese Resultate wurden außerdem durch immunologische Methoden sowie weitreichende proteomische Untersuchungen unterstützt, sodass die Basis zur Charakterisierung der Prozesse nach einer Rückenmarksverletzung geschaffen werden konnte. Diese ersten Ergebnisse wurden bereits erfolgreich publiziert, weitere Veröffentlichungen sind in Vorbereitung.
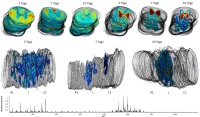
Graphische Darstellung der m/z-Werte 822,595 (oben links) und 844,518 (oben rechts) zu den drei gegebenen Zeitpunkten nach der Läsion, Visualisierung des m/z-Wertes 400,324 in den drei Rückenmarkssegmenten (R1 = rostral, L = Läsion, C1 = caudal) und zu den drei unterschiedlichen Zeitpunkten nach der Läsion (3, 7 und 10 Tage, Mitte) sowie das Mittelwertspektrum aller MALDI Imaging Daten (unten). Das Lipid mit der Masse 822,595 ist vornehmlich in der weißen Substanz lokalisiert, wohingegen das Lipid mit der Masse 844,518 die graue Substanz des Rückenmarks charakterisiert. Das Lipid mit der Masse 400,324 ist fast ausschließlich in der Läsionsstelle lokalisiert. Die Auswertung und Visualisierung erfolgte mit der Software SCiLS Lab 2016 von SCiLS, Zweigniederlassung der Bruker Daltonik GmbH (Bremen).