Räumlich dreidimensional aufgelöste Stoffwechsel-Analyse für die Medizin
| Arbeitsgruppe: | AG Technomathematik |
| Leitung: | Prof. Dr. Dr. h.c. Peter Maaß ((0421) 218-63801, E-Mail: pmaass@math.uni-bremen.de ) |
| Bearbeitung: |
Dr. Dennis Trede
Dr. Stefan Schiffler Sabine Eifeld (E-Mail: eifeld@math.uni-bremen.de ) |
| Projektförderung: | Wirtschaftsförderung Bremen WFB |
| Projektpartner: |
Bruker Daltonics GmbH Fraunhofer MEVIS , Fraunhofer MEVIS Helmholtz Zentrum München |
| Laufzeit: | 01.07.2010 - 30.06.2012 |
Die Entwicklung neuer Wirkstoffe und Therapien für die Medizin erfordert eine detaillierte Kenntnis über den Stoffwechsel (Metabolismus) des untersuchten Organismus. Auch bei der Krebsdiagnostik liefert der Stoffwechsel wichtige Informationen. Die klassischen tomographischen Verfahren wie die Computer-Tomographie oder histologische Färbetechniken bilden jedoch lediglich die Anatomie ab bzw. liefern nur partielle Informationen über den Stoffwechsel. Die komplette Metabolismus-Information ist dagegen im vollständigen Protein-Spektrum des Organismus enthalten, das über Verfahren der Massenspektrometrie bestimmt werden kann. Die klassischen Massenspektrometrie-Verfahren enthalten allerdings keinerlei Information über die räumliche Verteilung der Proteine.
Vor knapp zehn Jahren wurde mit der Entwicklung der sogenannten MALDI-Technik („Matrix-Assisted Laser Desorption/Ionization“) ein entscheidender Schritt geleistet, um die Massenspektrometrie zu einem 2D-bildgebenden Verfahren zu entwickeln: Durch diese Technik wurde es möglich, hoch präzise einzelne Gewebestellen zu markieren und das zugehörige Massenspektrum aufzunehmen. Mit dieser MALDI-Imaging-Technik erhält man erstmals räumlich zweidimensional aufgelöste Informationen über die Proteinstruktur in einzelnen Gewebeschnitten und somit detaillierte räumliche Informationen über den Stoffwechsel.
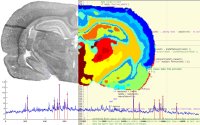
Der entstehende Datensatz enthält ca. 108 Messwerte, dessen Verarbeitung hoch spezialisierte, automatisierte Visualisierungs- und Auswerteroutinen verlangt. Gemeinsam mit dem Industriepartner Bruker Daltonik GmbH hat das Zentrum für Technomathematik bereits eine Methode entwickelt und zur Patentierung angemeldet, die den 2D-Schnitt in Segmente unterteilt, in denen ähnliche Stoffwechselvorgänge stattfinden. Dadurch ist es z.B. möglich, Proteine in dem zu analysierenden Gewebe zu identifizieren und bei der Krebsdiagnose zu berücksichtigen. Der wesentliche Schritt der entwickelten Methode ist die Rauschunterdrückung unter Berücksichtigung von örtlichen Informationen – eine mathematische Methode der morphologischen Bildverarbeitung. Die zweite Abbildung zeigt in der rechten Hälfte die metabolische Segmentierung des Gewebeschnitts mit der entwickelten Methode. In der linken Hälfte ist die Anatomie mithilfe eines mikroskopischen Fotos dargestellt.
In diesem Projekt soll ein Schritt weitergegangen werden: In enger Kooperation mit den Partnern werden aktuell technische Prozessketten entwickelt, um die bisherige 2D-MALDI-Technik zu einem 3D-bildgebenden Verfahren weiterzuentwickeln. Dies wird ermöglichen, das Protein-Spektrum eines gesamten Organs oder einer gesamten krankheitsbedingten Läsion in seiner vollen Komplexität zu erfassen und zu analysieren. Damit könnten beispielsweise wichtige klinisch-onkologische Fragestellungen direkt in Organen und Geweben erforscht werden, die den Kontext des hochkomplexen (heterogenen) 3D-Gewebeverbands voraussetzen. Dazu zählen die Verteilung und Metabolisierung von Wirkstoffen in den typischerweise sehr komplex aufgebauten, krankhaft veränderten Geweben (z.B. Tumoren) und das damit unmittelbar zusammenhängende Therapieansprechen, das mit einem 3D-MALDI-Imaging-Verfahren erstmals direkt in Organen und Geweben systembiologisch analysiert werden könnte.
Durch die zusätzliche dritte räumliche Dimension entstehen beim 3D-MALDI-Imaging Datensätze mit ca. 1010 Messwerten. Eine reine Darstellung der metabolischen 3D-Information ist zwar als technisches Problem von hoher Komplexität, es ist jedoch aus diagnostischer Sicht für sich genommen noch wenig aussagekräftig. Erst die Verknüpfung der metabolischen 3D-MALDI-Daten mit dreidimensionaler, anatomischer Information (z.B. mit Computer-Tomographie-Daten) erlaubt eine sinnvolle Auswertung dieser komplexen Daten. Die Aufgabe der Überlagerung beider Volumendatensätzen, die durch diese unterschiedlichen Aufnahmetechniken generiert sind, liegt dem Problem der Bildregistrierung zugrunde. Das Ergebnis wird ein hochdimensionales Bild sein, das die Informationen beider Bildgebungsverfahren kombiniert, d.h. sowohl den Stoffwechsel als auch die Anatomie visualisiert.

